細胞が分裂する前には、まず全ての染色体を複製し、それぞれの娘細胞が完全な遺伝情報を受け取れるようにする必要があります。これまで科学者たちは、分裂が起こると、ゲノムは通常形成している特徴的な3D内部構造を失うと信じていました。分裂が完了すると、ゲノムは徐々にその複雑な球状の構造を取り戻し、これが特定の細胞でどの遺伝子をオンにするかを制御する上で不可欠な役割を果たすと考えられていたのです。しかし、MITによる新しい研究は、この見解が完全には正確ではないことを示しています。より高解像度のゲノムマッピング技術を用いて、研究チームは、調節エレメントと遺伝子をつなぐ小さな3Dループが、細胞分裂、すなわち有糸分裂の間もゲノム内に存続していることを発見しました。
「この研究は、私たちが有糸分裂をどう考えるべきかを明確にするのに本当に役立ちます。かつて有糸分裂は、転写も遺伝子活性に関連する構造もない『白紙の状態』と考えられていました。しかし今、私たちはそれが完全には正しくないことを知っています」と、MITの生物工学准教授であるアンダース・セイル・ハンセン博士(Anders Sejr Hansen, PhD)は述べています。「私たちが見ているのは、そこには常に構造があるということです。それは決してなくなりません。」
研究者たちはまた、これらの調節ループが、細胞分裂の準備のために染色体がよりコンパクトに凝縮する際に、むしろ強化されるように見えることも発見しました。この凝縮によって遺伝的な調節エレメントが互いに近くなり、くっつき合うことが促進されます。これは、細胞がひとつの細胞周期に存在した相互作用を「記憶」し、次の周期に持ち越すのを助けている可能性があります。
「この発見は、ゲノムの構造と、遺伝子のオン・オフを管理するというその機能とを結びつける助けとなります。これは、この分野で数十年にわたる未解決の課題でした」と、この研究の筆頭著者であるヴィラート・ゴエル博士(Viraat Goel, PhD)は語ります。
ハンセン博士と、MIT医学工学科学研究所のリサーチサイエンティストであるエドワード・バニガン博士(Edward Banigan, PhD)が、2025年10月17日に Nature Structural and Molecular Biology 誌に掲載されたこの論文の上級著者です。MIT医学工学科学研究所および物理学科の教授であるレオニード・ミルニー博士(Leonid Mirny, PhD)、およびペンシルベニア大学ペレルマン医学大学院の教授であるガード・ブロベル医学博士(Gerd Blobel, MD)も、この研究の著者です。このオープンアクセス論文のタイトルは「「Dynamics of Microcompartment Formation at the Mitosis-to-G1 Transition(有糸分裂からG1期への移行におけるマイクロコンパートメント形成のダイナミクス)」」です。
驚くべき発見
過去20年間で、科学者たちは細胞核内でDNAがそれ自体を3Dループに組織化することを発見してきました。多くのループは、互いに何百万塩基対も離れている可能性のある遺伝子と調節領域との間の相互作用を可能にしますが、他のループは細胞分裂中に染色体を凝縮させるために形成されます。
これらの3D構造のマッピングの多くは、マサチューセッツ大学チャン医学校のジョブ・デッカー博士(Job Dekker, PhD)が率い、MITの研究者も含むチームによって最初に開発されたHi-Cと呼ばれる技術を用いて行われてきました。Hi-Cを行うために、研究者たちは酵素を使ってゲノムを多くの小さな断片に切り刻み、細胞核内の3D空間で互いに近くにある断片を生化学的に連結します。その後、それらをシーケンシングすることによって、相互作用している断片の正体を突き止めます。
しかし、その技術では、エンハンサーのような調節エレメントと遺伝子との間の特異的な相互作用をすべて選び出すには、解像度が十分に高くありません。エンハンサーとは、遺伝子のプロモーター(転写が開始される部位)に結合することで、その遺伝子の転写を活性化するのを助けることができる短いDNA配列です。
2023年、ハンセン博士らは、以前可能だったよりも100倍から1,000倍高い解像度で3Dゲノム構造を分析できる新しい技術を開発しました。この技術は「リージョンキャプチャーMicro-C(RC-MC: Region-Capture Micro-C)」として知られ、ゲノムを類似したサイズの小さな断片に切断する異なる酵素を使用します。また、ゲノムのより小さなセグメントに焦点を当てることで、標的ゲノム領域の高解像度3Dマッピングを可能にします。
この技術を用いて、研究者たちはこれまで見られなかった新しい種類のゲノム構造を特定し、それを「マイクロコンパートメント」と名付けました。これらは、互いに近くに位置するエンハンサーとプロモーターがくっつき合うときに形成される、高度に連結した微小なループです。
その論文では、これらのループが他のゲノム構造を形成するのと同じメカニズムでは形成されないことが実験で明らかになりましたが、研究者たちはそれらが正確にどのように形成されるかを突き止めることはできませんでした。その疑問に答えることを期待して、チームは細胞が細胞分裂を経る過程を研究することに着手しました。
有糸分裂中、染色体は2つの娘細胞間で複製され、分類され、分配されるために、はるかにコンパクトになります。これが起こると、A/Bコンパートメントや「トポロジカル関連ドメイン(TADs: topologically associating domains)」と呼ばれるより大きなゲノム構造は完全に消失します。
研究者たちは、自分たちが発見したマイクロコンパートメントも有糸分裂中に消失するだろうと信じていました。細胞分裂プロセス全体を通じて細胞を追跡することにより、彼らは有糸分裂が完了した後にマイクロコンパートメントがどのように現れるかを解明したいと考えていました。
「有糸分裂中は、ほぼすべての遺伝子転写が停止すると考えられてきました。そして私たちの論文以前は、遺伝子調節に関連するすべての3D構造が失われ、凝縮に置き換わるとも考えられていました。それは細胞周期ごとの完全なリセットです」とハンセン博士は言います。
しかし、驚いたことに、研究者たちはマイクロコンパートメントが有糸分裂中にも依然として見られること、そして実際には、細胞が細胞分裂を経るにつれてそれらがより顕著になることを発見しました。
「私たちは、まあ、確かに分かっている唯一のことは、有糸分裂中には調節構造が存在しないということだ、と考えてこの研究に入りました。それから偶然、有糸分裂中に構造を発見したのです」とハンセン博士は語ります。
彼らの技術を用いて、研究者たちはまた、A/BコンパートメントやTADsのようなより大きな構造が、以前に見られていたように、有糸分裂中に消失することも確認しました。
「この研究は、RC-MCアッセイの前例のないゲノム解像度を活用して、従来の「3Cベースのアッセイ(3C-based assays)」を用いてきた過去には見落としていた、有糸分裂時のクロマチン構成に関する新しく驚くべき側面を明らかにしています。著者らは、有糸分裂中のTADsやコンパートメント化のよく知られた劇的な喪失とは対照的に、微細な『マイクロコンパートメント』、すなわち活性調節エレメント間のネストした相互作用が、維持されるか、あるいは一時的に強化されることさえあることを明らかにしています」と、この研究には関与していないワイルコーネル医科大学の分子生物学准教授であるエフィー・アポストロウ医学博士(Effie Apostolou, MD)は述べています。
転写の急増
この発見は、有糸分裂の終わり近くで通常起こる遺伝子転写の急増(スパイク)についての説明を提供するかもしれない、と研究者たちは言います。1960年代以来、有糸分裂中は転写が完全に停止すると考えられていましたが、2016年と2017年のいくつかの研究で、細胞は短時間の転写スパイクを経験し、それは細胞が分裂を終えるまですぐに抑制されることが示されました。
今回の新しい研究で、MITのチームは、有糸分裂中、マイクロコンパートメントは細胞分裂中にスパイクする遺伝子の近くで見つかる可能性が高いことを発見しました。彼らはまた、これらのループが有糸分裂中に起こるゲノムの凝縮の結果として形成されるように見えることも発見しました。この凝縮がエンハンサーとプロモーターをより接近させ、それらがくっつき合ってマイクロコンパートメントを形成することを可能にします。
一度形成されると、マイクロコンパートメントを構成するループは、ある程度「偶然に」遺伝子転写を活性化する可能性があり、それはその後、細胞によって停止されます。細胞が分裂を終え、「G1期」として知られる状態に入ると、これらの小さなループの多くは弱まるか消失します。
「有糸分裂中のこの転写スパイクは、有糸分裂中にマイクロコンパートメントが形成されるための特異的に有利な環境が生じることから生じる、望ましくない事故のようにさえ思えます」とハンセン博士は言います。「そして、細胞はG1期に入ると、それらのループの多くを速やかに剪定し、取り除きます。」
染色体の凝縮は細胞のサイズや形状にも影響され得るため、研究者たちは現在、それらの特徴の変動がゲノムの構造、ひいては遺伝子調節にどのように影響するかを調査しています。
「私たちは、細胞が形状やサイズを変えるいくつかの自然な生物学的状況について考えており、以前は説明がつかなかったいくつかの3Dゲノムの変化を説明できるかもしれません」とハンセン博士は言います。「もう一つの重要な問いは、G1期に入ったときに、遺伝子発現の忠実性を確保するために、細胞はどのマイクロコンパートメントを保持し、どのマイクロコンパートメントを除去するかを、どのようにして選んでいるのかということです。」
この投稿は、MIT News の Anne Trafton 氏によるリリースに基づいています。
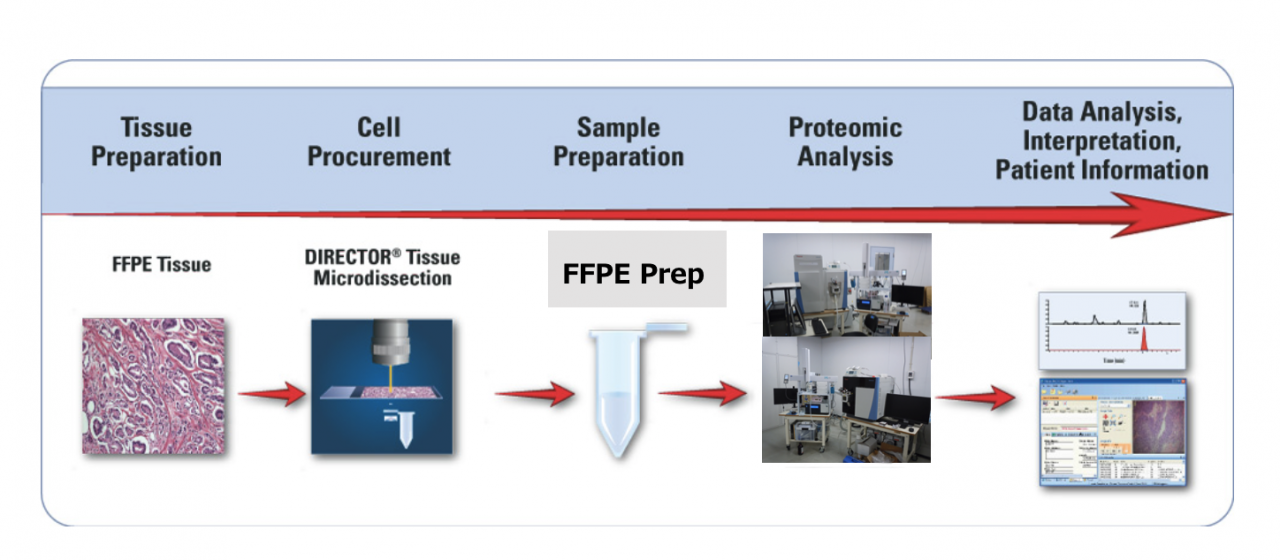
画像:MITの実験により、ゲノムの3次元構造内に黄色で示された「マイクロコンパートメント」の存在が明らかになった。これらのコンパートメントは微小なループによって形成され、遺伝子調節に関与している可能性がある。 (Credit: Ed Banigan, edited by MIT News)
[News release] [Nature Structural & Molecular Biology article]